宏基因组实战10. 绘制圈图-Circos安装与使用
看教程不够直观,那就看视频吧! >>点击加载视频
前情提要
如果您在学习本教程中存在困难,可能因为缺少背景知识,建议先阅读本系列前期文章
- 宏基因组分析理论教程
- 微生物组入门圣经+宏基因组分析实操课程
- 1背景知识-Shell入门与本地blast实战
- 2数据质控fastqc, Trimmomatic, MultiQC, khmer
- 3组装拼接MEGAHIT和评估quast
- 4基因注释Prokka
- 5基于Kmer比较数据集sourmash
- 5基于Kmer比较数据集sourmash
- 6不比对快速估计基因丰度Salmon
- 7bwa序列比对, samtools查看, bedtools丰度统计
- 8分箱宏基因组binning, MaxBin, MetaBin, VizBin
- 9组装assembly和分箱bin结果可视化—Anvi'o
- MetaPhlAn2分析有参宏基因组
Circos安装与使用
Circos是不款功能强大的可视化软件,可以使用环状图形展示基因数据比较。可以添加多种图展信息,如热图、散点图等。
本教程目标:
- 在Ubuntu上安装circos
- 可视化宏基因组数据
注: 除了本文的简短教程,circos官网有非常详细的教程
安装Circos
sudo apt-get -y install libgd-perl wd=~/test/metagenome17 cd $wd mkdir circos cd circos curl -O http://dib-training.ucdavis.edu.s3.amazonaws.com/metagenomics-scripps-2016-10-12/circos-0.69-3.tar.gz tar -xvzf circos-0.69-3.tar.gz # 安装模块 circos -modules > modules grep missing modules |cut -f13 -d " " > missing_modules for mod in $(cat missing_modules); do sudo cpan install $mod; done # 检查模块是否安装好,全部出现OK则全部安装成功 circos -modules # 运行演示数据 cd $wd/circos/circos-0.69-3/example bash run
Use of uninitialized value in join or string at /mnt/bai/yongxin/test/metagenome17/circos/circos-0.69-3/bin/../lib/Circos/Heatmap.pm line 75. 上面报错信息,但并没有影响结果生成 将会产生``circos.png`
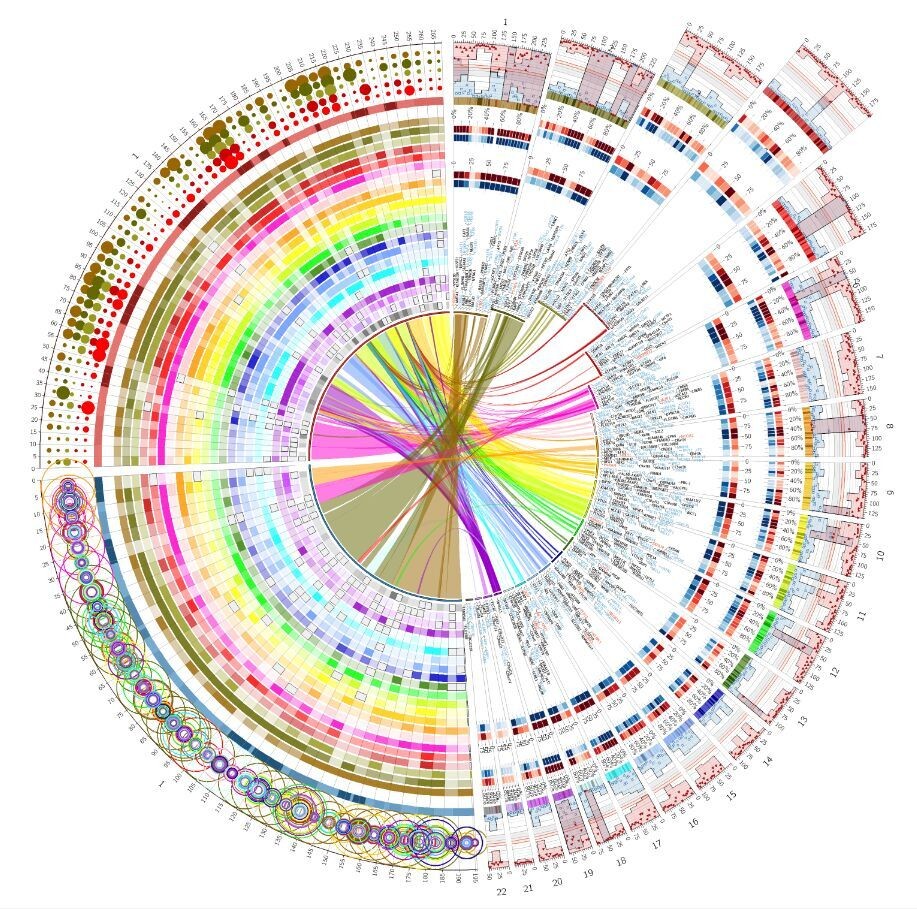
可视化基因覆盖度和方向
mkdir ${wd}/circos/plotting
cd ${wd}/circos/plotting
# 链接prokka注释文件,salmon定量文件
ln -fs ${wd}/annotation/prokka_annotation/metagG.gff .
ln -fs ${wd}/annotation/final.contigs.fa .
ln -fs ${wd}/quant/*.counts .
# 下载脚本辅助绘图
curl -L -O https://github.com/ngs-docs/2016-metagenomics-sio/raw/master/circos-build.tar.gz
tar -xvzf circos-build.tar.gz
curl -L -O https://s3-us-west-1.amazonaws.com/dib-training.ucdavis.edu/metagenomics-scripps-2016-10-12/subset_assembly.fa.gz
gunzip subset_assembly.fa.gz
# 上步无法下载可翻墙或从上节位置复制 cp $wd/anvio-work/subset_assembly.fa .
mv subset_assembly.fa final.contigs.fa
使用khmer包提取长contigs可视化(太多人类不可读)
# 进入python3虚拟环境
. ~/py3/bin/activate
extract-long-sequences.py final.contigs.fa -l 24000 -o final.contigs.long.fa
# 生成circos需要的文件
python parse_data_for_circos.py
python2.7.12报错File "/usr/local/lib/python2.7/dist-packages/pandas/core/indexing.py", line 1390, in error (key, self.obj._get_axis_name(axis))) KeyError: 'the label [count] is not in the [index]'
python3.5.2报错信息 KeyError: 'the label [count] is not in the [index]' 脚本应该是好脚本,只是不知道那里出了错。
# 手动运行脚本 mkdir -p org_gff grep '>' final.contigs.long.fa |cut -f1 -d ' '|cut -f2 -d '>' > org_list "for org in `cat org_list`; do grep -w $org metagG.gff > $org.subset.gff; done mv *subset.gff org_gff # 后面只有不多的python代码,只是我看不懂了,大神来帮忙看看问题吧parse_data_for_circos.py
Circos主要操作三类文件:
- 配置文件,包括样式和输出的图
- 核型文件,定义染色体大小布局
- 图中的具体配置属性
上面的脚本产生核形文件和另外四个文件,它们都是什么,从那来的吗?
我们进入circos-build并打``circos`:
cd circos-build circos
此命令会产生circos.svg and circos.png看结果吧。
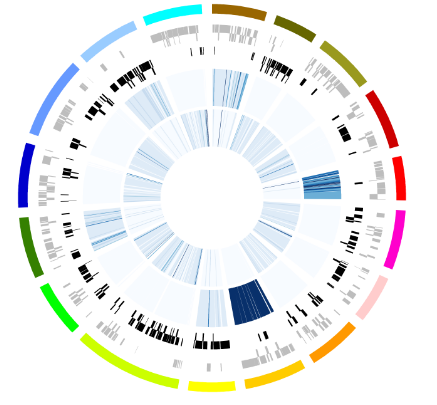
我们仔细看一下circos.config,可以按帮助尝试修改,如颜色、半径 大小,看看有那些变化?
参考文献
- 英文版 https://2017-cicese-metagenomics.readthedocs.io/en/latest/circos_tutorial.html
- 文章链接 http://genome.cshlp.org/content/early/2009/06/15/gr.092759.109.abstract
- 官方教程 http://circos.ca/documentation/tutorials
- 官方课程 http://circos.ca/documentation/course/
猜你喜欢
- 一文读懂:1微生物组 2进化树 3预测群落功能
- 热文:1图表规范 2DNA提取 3 实验vs分析
- 必备技能:1提问 2搜索 3Endnote
- 文献阅读 1热心肠 2SemanticScholar3geenmedical
- 扩增子分析:1图表解读 2分析流程 3统计绘图 4群落功能 5进化树
- 科研团队经验:1云笔记 2云协作 3公众号
- 系列教程:1Biostar 2微生物组 3宏基因组
- 生物科普 1肠道细菌 2生命大跃进 3细胞的暗战 4人体奥秘
- 发表于 2017-11-22 23:37
- 阅读 ( 8456 )
- 分类:其他组学
你可能感兴趣的文章
- 央视与遗传发育所合拍《走进科学-小菌株大作为》——枯草芽孢杆菌替代畜牧业抗生素添加 7664 浏览
- 16S+功能预测也能发Sciences:尸体降解过程中的微生物组 9124 浏览
- R画月亮阴晴圆缺:corrplot绘图相关系数矩阵 15841 浏览
- Cell:人体细菌到究竟有多少,再作报告必引此文 10398 浏览
- R语言添加p-value和显著性标记 17648 浏览
- ggalluvial:冲击图展示组间变化、时间序列和复杂多属性alluvial diagram 13415 浏览
