如何极其简单的使用GEO数据来做差异分析
看教程不够直观,那就看视频吧! >>点击加载视频
新版本DECenter使用看这里:https://www.shengxin.ren/article/207
无论你是要看某个基因是否差异表达或者筛选某个GEO数据集的差异基因,这个方法绝对能够帮助你事半功倍
首先假设你已经找到了一套数据GSE32323
这套数据共包含44个样本,其中有17个配对的癌与癌旁样本
我们先下载数据,如图
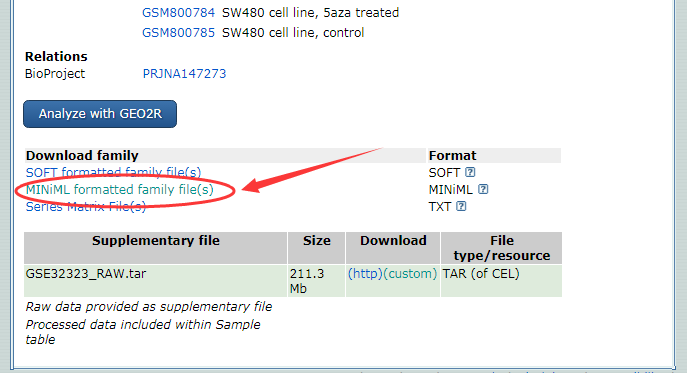 然后使用GEO芯片数据转换器提取出表达矩阵和样本信息表 (不会提看这里)如图:
然后使用GEO芯片数据转换器提取出表达矩阵和样本信息表 (不会提看这里)如图:
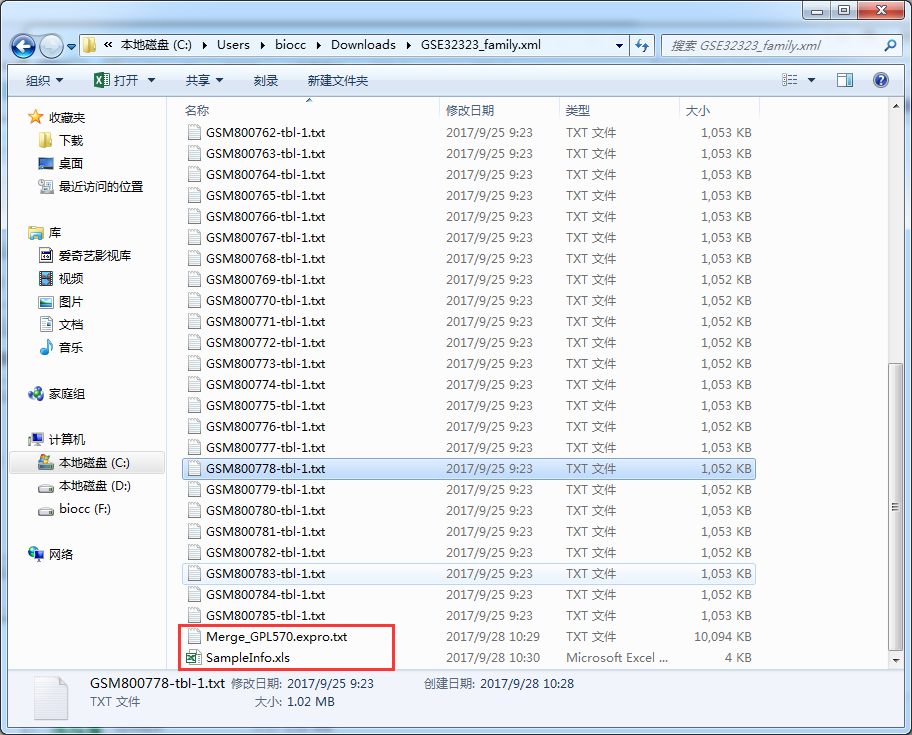
打开SampleInfo.xls文件编辑样本顺序和分组
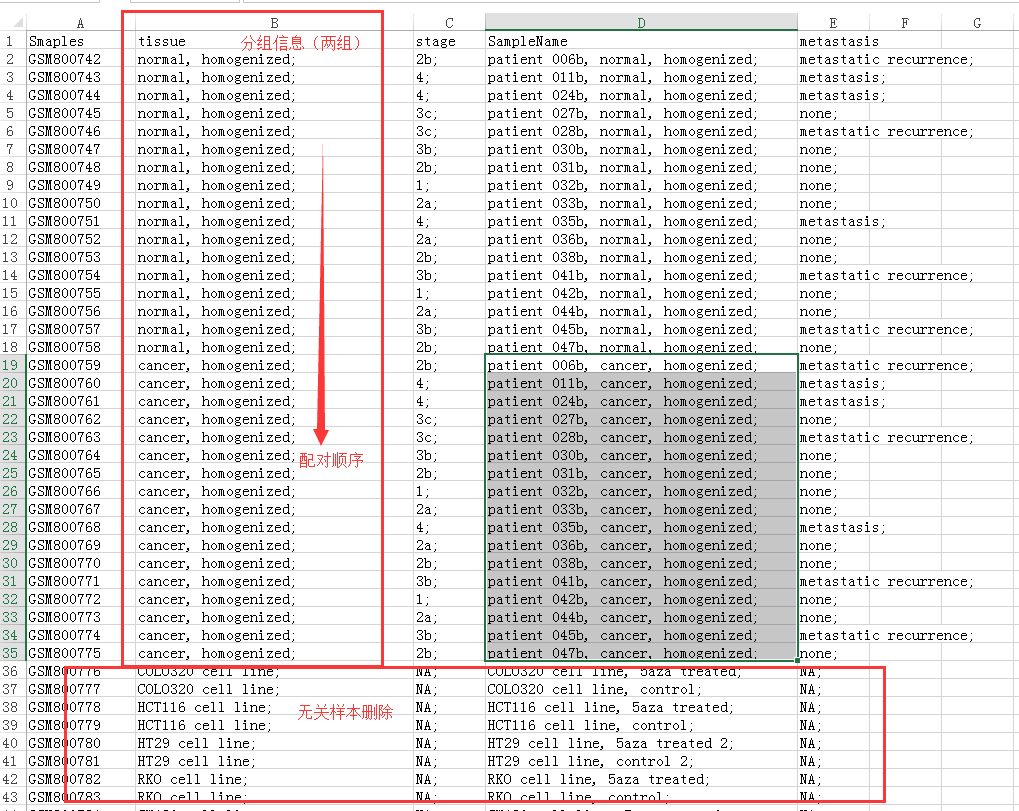 最终修改后的样本信息表为(为什么cancer排在前面?软件默认前面比后面啊):
最终修改后的样本信息表为(为什么cancer排在前面?软件默认前面比后面啊):
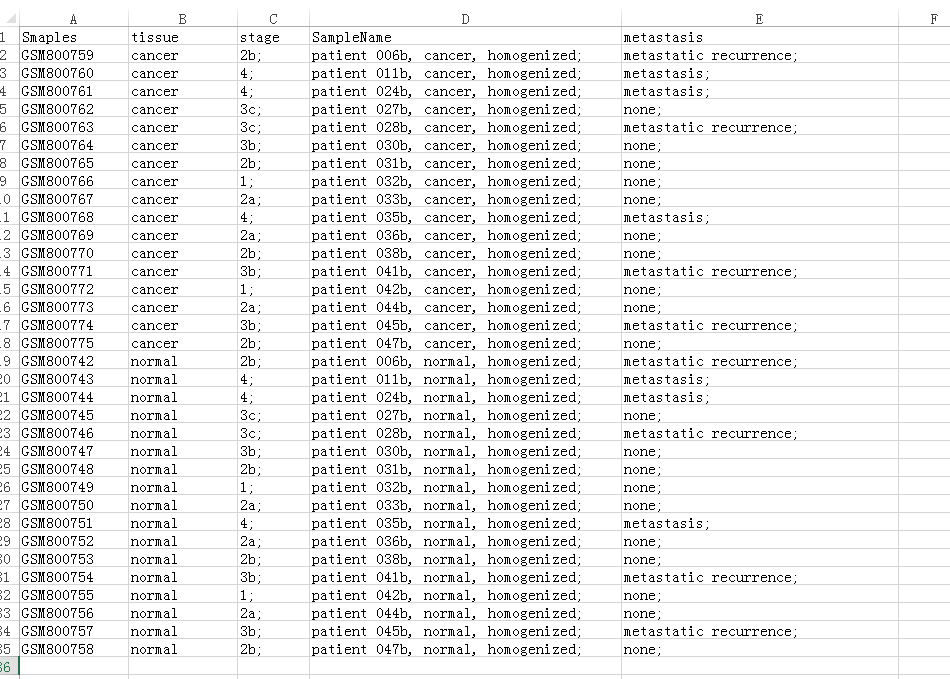
然后使用DECenter(下载链接:http://gap.shengxin.ren/tool/10/)进行差异分析
打开,长这个样子
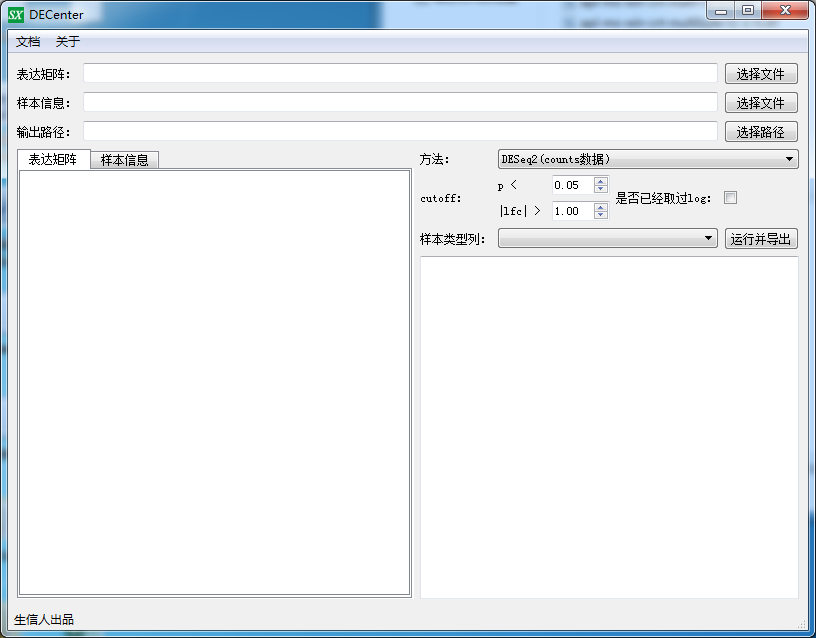
看似需填项比较多,其实无非就四步
1、选择表达矩阵
2、选择样本信息表(因为你要告诉软件怎么分组的嘛)
3、选择筛选差异的方法,如果是芯片数据当然选择limma了,如果是RNA-Seq的counts数据,选择DESeq2或者edgR也行啊
4、选择样本分组列,然后选择结果保存目录点击运行就行了
示例如下:
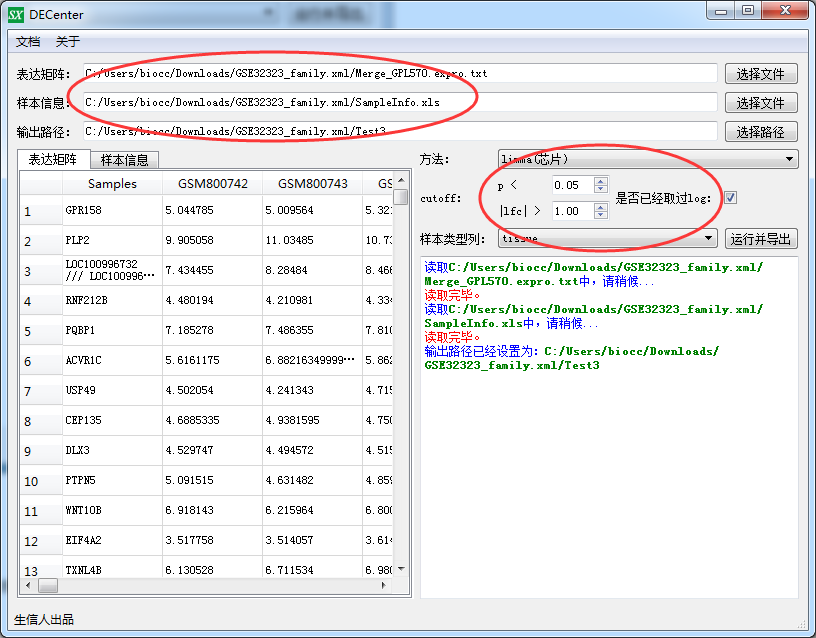 等提示跑完,打开结果保存的目录
等提示跑完,打开结果保存的目录
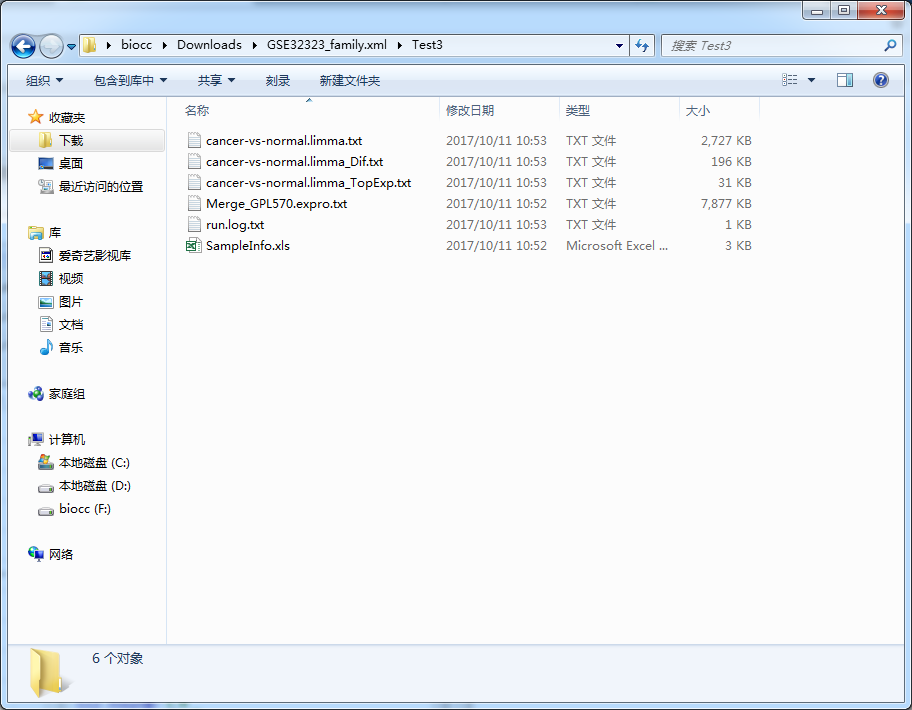 总共得到三个文件
总共得到三个文件
1、cancer-vs-normal.limma.txt:这是cancer比normal的所有基因差异结果
2、cancer-vs-normal.limma_Dif.txt:这是根据咱们在软件选择的阈值筛选之后的差异结果
3、cancer-vs-normal.limma_TopExp.txt:这是提取的最差异的基因的表达谱
得到了差异结果之后,我们要对结果进行一个展示吧
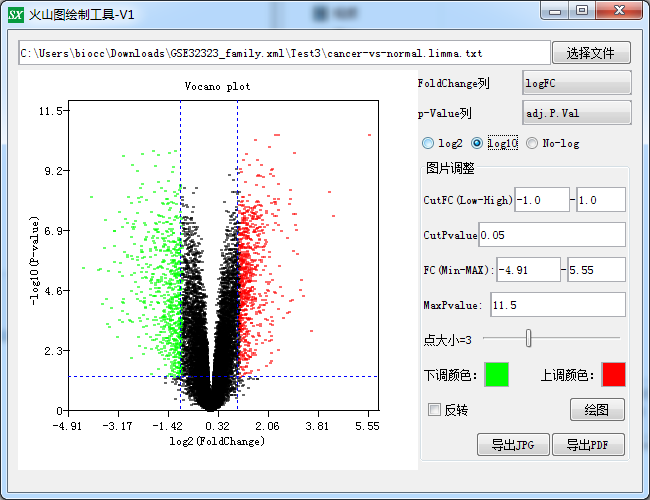
先拿cancer-vs-normal.limma.txt使用火山图制作工具做个火山图,教程看这里:https://www.shengxin.ren/article/174
 再拿cancer-vs-normal.limma_TopExp.txt使用热图绘制工具画个热图:教程看这里:https://www.shengxin.ren/article/165
再拿cancer-vs-normal.limma_TopExp.txt使用热图绘制工具画个热图:教程看这里:https://www.shengxin.ren/article/165
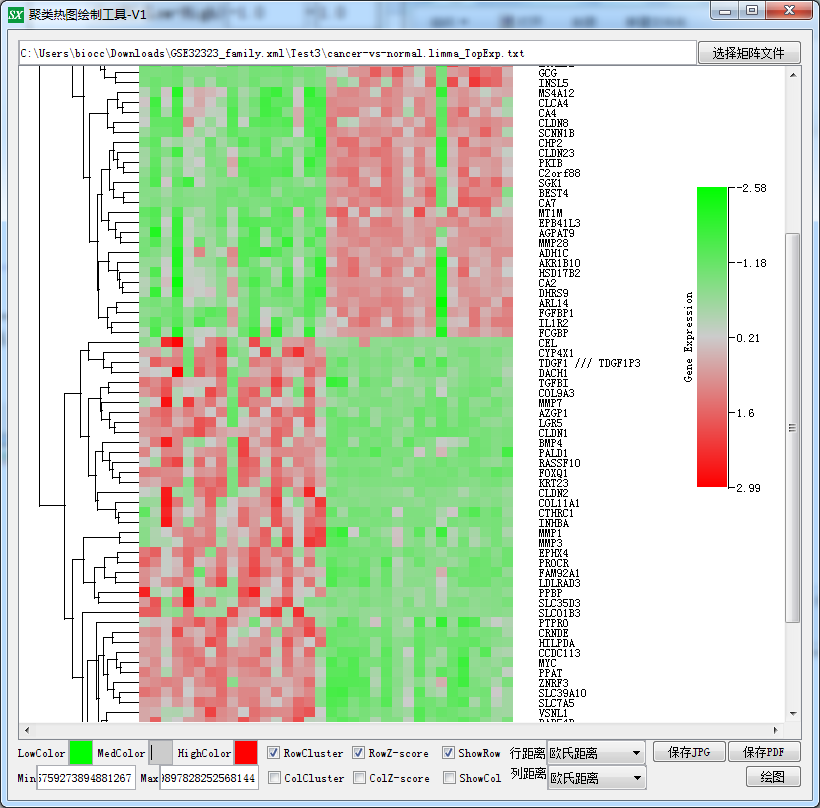 导出图片,放到PPT中就可以向老板汇报了
导出图片,放到PPT中就可以向老板汇报了
- 发表于 2017-09-28 10:48
- 阅读 ( 77173 )
- 分类:软件工具
你可能感兴趣的文章
- limma快速差异分析工具 7958 浏览
- 转录组Count数据差异分析工具 7172 浏览
- 快速差异分析工具——limma包 25847 浏览
- limma快速差异分析工具! 8120 浏览
- limma的两个弟弟:edgeR和DESeq2 8346 浏览
- 在GEO数据库如何找带有预后信息的数据?一分钟搞定,适用于找任何的样本特征数据 21051 浏览
